

|
单细胞测序技术服务 靶向单细胞测序(lncRNA&mRNA) 单细胞测序 |
|
生物分子凝聚体研究 HyPro靶RNA临近标记技术 |
|
NGS测序技术服务 环状DNA测序(eccDNA测序) |
|
Ribo-seq Ribo seq(ribosome profiling) |
核糖体-新生肽链复合物(RNC) RNC联合 circRNA芯片 RNC联合 lncRNA芯片 RNC-seq |
|
蛋白表达定量 DIA定量蛋白质组学 Label free非标定量 TMT标记定量 PRM靶向定量 |
蛋白修饰定量 N-糖基化蛋白组学 乳酸化修饰蛋白质组学 O-GlcNAc修饰蛋白质组学 |
microRNA(miRNA)属于small ncRNAs,是一类大小为21-23nt的单链短RNA分子。miRNA是基因表达的主要调节分子。miRNA以序列互补配对的方式与特异靶mRNA 的3’UTR结合,通过降解靶mRNA或抑制其蛋白翻译调控基因的表达。miRNA不但在基本的生物学过程,如发育、应激反应、代谢和基因组完整性维持等方面有基本而重要的调控作用;在疾病的发生发展全过程中,也发挥着重要的调控作用。
安捷伦(Agilent)公司凭借先进的芯片生产工艺开发出高性能miRNA芯片平台,该平台结合了独特的miRNA直接标记方法以及利用创新的SurePrint喷墨合成技术设计探针等优点,同时基于miRBase 21.0数据库,具有高特异性和高灵敏度的特点,能特异性地检测成熟体miRNA,并能有效区分序列高度相似的不同miRNA,可广泛应用于多种类型样品miRNA表达的检测,准确的阐明miRNA在研究中的重要作用,国内外利用该平台已经发表了大量文章。
Aksomics(原康成生物)为您提供Agilent miRNA表达谱芯片技术服务,您只需要提供保存完好的组织或细胞标本,Aksomics的芯片技术服务人员就可为您完成全部实验操作,并提供完整的实验报告。同时,根据您的研究需要,Aksomics 还提供多平台联合分析、分子标志物筛选分析等各种深入数据挖掘服务。
| 芯片名称 | 物种 | P/N | Design ID | 规格 | 描述 |
|---|---|---|---|---|---|
| Agilent Human miRNA Microarray, Release 21.0 | 人类 | G4872A | 070156 | 8 x 60K | 2,549 human miRNAs represented miRBase database (Release 21.0) Agilent 60-mer SurePrint technology |
| Mouse miRNA Microarray, Release 21.0 | 小鼠 | G4872A | 070155 | 8 x 60K | 1,881 mouse miRNAs represented miRBase database (Release 21.0) Agilent 60-mer SurePrint technology |
| Rat miRNA Microarray, Release 21.0 | 大鼠 | G4471A | 070154 | 8 x 15K | 758 rat miRNAs represented miRBase database (Release 21.0) Agilent 60-mer SurePrint technology |
1.创新的标记系统和探针设计:高效的直接标记方法,独特的SurePrint原位喷墨合成技术合成60-mer寡核苷酸探针,可以方便的区分成熟miRNA和miRNA前体,同时可以为序列高度相似的不同miRNA检测提供高的灵敏度和特异性。
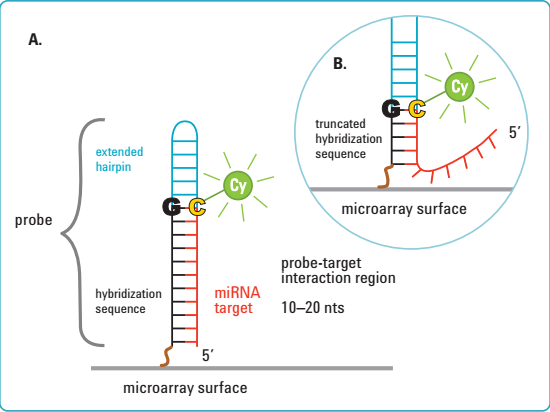
Components of the Agilent miRNA microarray probe design
2.数据来源于miRBase 21.0,芯片数据更新迅速,为客户提供前沿的miRNA研究信息。
3.灵敏度高,只需100ng的Total RNA即可用来进行标记实验。
4.动态范围广,检测丰度跨4个数量级,有利于检测到更宽丰度范围的miRNA。
5.样品适用范围广。
6.灵活方便的定制服务。
1.样品RNA抽提
2.RNA质量检测
3.制备荧光标记探针,miRNA 3’端进行Cy荧光标记,采用SurePrint原位喷墨合成技术合成60-mer用于与芯片杂交的荧光探针。
4.芯片杂交,取一定量的质检达标样本,与miRNA芯片进行杂交。
5.图像采集和数据分析。
6.提供实验报告—包括详细的实验方法和芯片实验数据及图表。
Aksomics miRNA芯片技术服务基本数据分析结果展示
1. miRNA差异表达数据
通过芯片中位值对miRNA芯片原始信号值进行标准化。通过标准化信号值计算出每个miRNA在不同样品间的表达变化(fold change),并通过t-test计算样品间miRNA表达量显著性p值。针对多重比较,p值被校正为FDR。根据倍数变化,p值或者FDR等参数筛选差异表达的miRNA。
适用范围:两个或两组样品间的比较,建议每组样品数目大于或等于3。
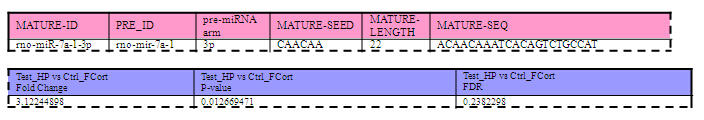
图释:样品间差异表达的miRNA数据示例。
2. 差异表达miRNA的聚类图
层次聚类是一种最常见的用于分析表达数据的聚类方法。它可以根据样品中基因的表达水平将样品自动的分组,可以让客户从整体上评估样品间的基因表达差异,以及样品间的关系。左侧的树状图可以反映样品间基因表达模式的关系。
适用范围:两组或多组样品的miRNA表达谱分析
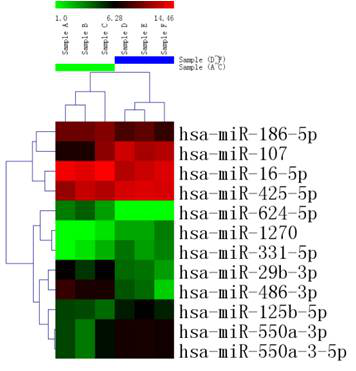
图释:不同样品组之间差异表达miRNA的聚类示例。
3. 差异表达miRNA的火山图
火山图可以对不同样品组之间差异表达的miRNA进行图形化的展示,直观的展示miRNA在样品组间的倍数变化与相应的统计学显著性之间的关系。横轴代表差异miRNA表达倍数的变化(log2转化),纵轴代表相应的p值(-log10转化)。
适用范围:两组样品间的差异miRNA分析,每组样品数目必须大于等于3。
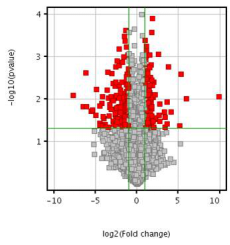
图释:火山图示例。
Aksomics miRNA芯片技术服务高级数据分析结果展示
1.差异表达miRNA的靶基因预测及miRNA-靶基因网路图构建
Aksomics通过三大数据库(miranda, mirbase, targetscan)预测miRNA靶点信息,将三种数据库的结果交集作为最终miRNA的靶基因结果,有效的降低了靶基因预测的假阳性率。Venn图展示了对于特定miRNA列表利用上述数据库的多个预测结果的整合分析。同时构建了miRNA-靶基因的网络图,直观的展示miRNA及其靶基因的调控关系。
适用范围:两组或多组数据比较获得的差异miRNA,一般情况下用于网络分析的miRNA数目应小于10个。
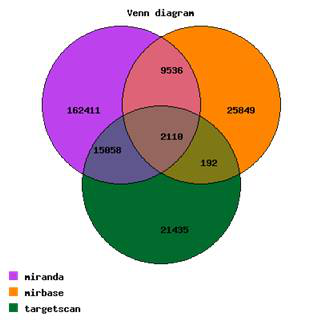
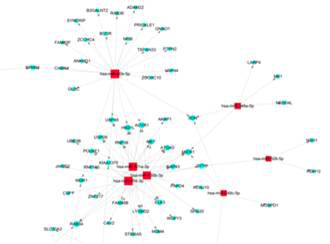
图释:上图:Aksomics miRNA靶基因预测结果的Venn图示例;下图:Aksomics miRNA—靶基因网络图示例。
2.靶基因的功能分析:Go & Pathway分析
为了获得对miRNA生物学功能的理解,鉴定其全部靶mRNA(靶基因)是必不可少的。Aksomics使用多种数据库来预测miRNA靶基因。之后对这些基因的功能进行分析(GO分析和KEGG pathway分析)。
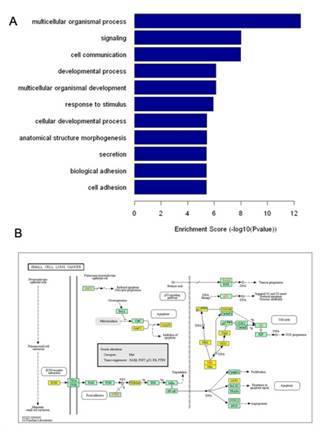
图释:A. GO分析结果展示:预测的差异表达miRNA靶基因的前10个富集生物学过程;B. Pathway分析结果展示:预测的miRNA靶基因(黄色标注)富集到的细胞周期相关通路。
Aksomics miRNA芯片与其它产品联合数据分析结果展示
1.miRNA芯片与lncRNA/circRNA芯片结果联合分析(ceRNA Analysis)
Aksomics通过MuTaMe(mutually targeted MRE enrichment )分析寻找我们感兴趣的lncRNA/circRNA的ceRNAs,进而构建miRNA、lncRNA/circRNA和mRNA的调控网络,从而揭示ceRNA通过竞争性结合miRNA来调控目的lncRNA/circRNA的新的调控模式。
适用范围:同时具有miRNA芯片数据和lncRNA/circRNA芯片数据的样品。
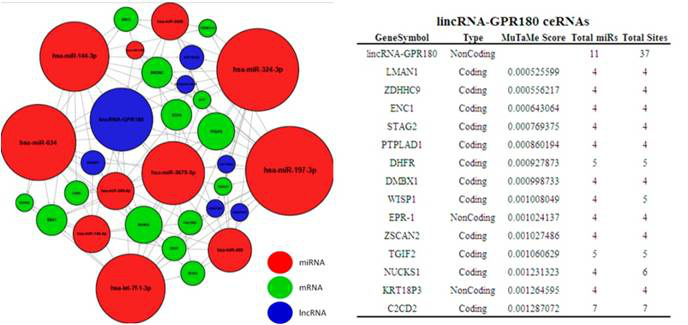
图释:ceRNA分析结果展示。左侧:ceRNA网络图。右侧:针对网络图中的特定lncRNA/circRNA(lincRNA-GPR180)的lncRNA/circRNA-miRNA-mRNA相互作用详细信息。
2.miRNA芯片与mRNA芯片结果联合分析
根据表达谱芯片结果和miRNA芯片结果联合分析,进一步定位差异miRNA发挥功能的途径以及相应的差异表达靶基因可能引起的生物学通路变化。
适用范围:同时具有mRNA表达谱数据和miRNA表达谱数据的样品,一般情况下用于分析的差异miRNA数目应小于10个。
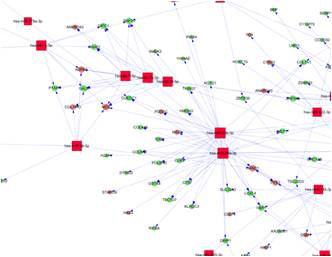
图释:Aksomics miRNA芯片与mRNA芯片联合分析示例:miRNA-靶基因网络图。
3.miRNA与DNA甲基化芯片结果联合分析
DNA甲基化和miRNA调控是两种重要的表观遗传现象。研究表明,特定miRNA能够作为肿瘤抑制miRNA靶向DNA甲基转移酶。联合miRNA和DNA甲基化芯片结果能够研究两者之间的复杂调控关系,更好地理解癌症发生的机制。
适用范围:同时具有miRNA表达谱数据和甲基化谱数据的样品。
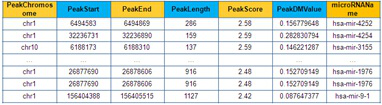
筛选评估原发性骨关节炎(OA)风险和进展的潜在miRNA生物标志物(Serum microRNA array analysis identifies miR-140-3p, miR-33b-3p and miR-671-3p as potential osteoarthritis biomarkers involved in metabolic processes. Clin Epigenetics,2017)
骨关节炎(OA)是最常见的慢性退行性关节病,是导致疼痛和残疾的主要原因。了解OA发病机制涉及的分子机制对于OA个性化治疗的发现是必不可少的。然而,早期检测疾病缺乏以及开发有效的OA治疗仍然是一个主要挑战。迄今为止,OA疾病诊断和严重程度判断的标准方法是X线片,似乎仅限于疾病晚期的检测,并且在监测疾病进展方面有弱点。因此,无创和敏感的血清生物标志物的鉴定将有助于OA的诊断,预后和早期治疗,
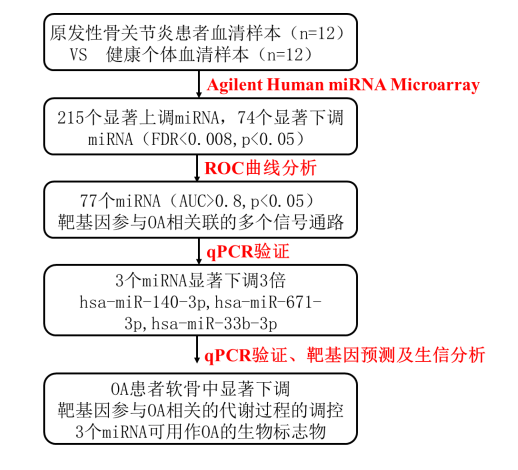
在这项研究中,我们的目标是确定OA患者的miRNA生物标志物。我们使用Agilent Human miRNA Microarray在12名原发性OA患者血清中鉴定出279个差异表达的miRNA。 ROC分析显示77个miRNA的AUC> 0.8,p <0.05。对77种miRNA进行生物信息学分析表明,它们的靶基因参与了与OA相关联的多个信号通路。选择7个排名靠前的miRNA在OA患者的血清中进行qRT-PCR验证,发现3个显著下调3倍的miRNA(hsa-miR-33b-3p, hsa-miR-671-3p和hsa-miR-140-3p),靶基因分析表明,InsR和IGFR1是3个miRNA的共同靶基因,它们主要参与OA相关的代谢过程的调控。最终表明我们在OA患者的血清中鉴定了三个miRNA(hsa-miR-140-3p,hsa-miR-671-3p和hsa-miR-33b-3p)可以用作评估的OA风险和进展的一个潜在的生物标志物。
技术路线
结果展示
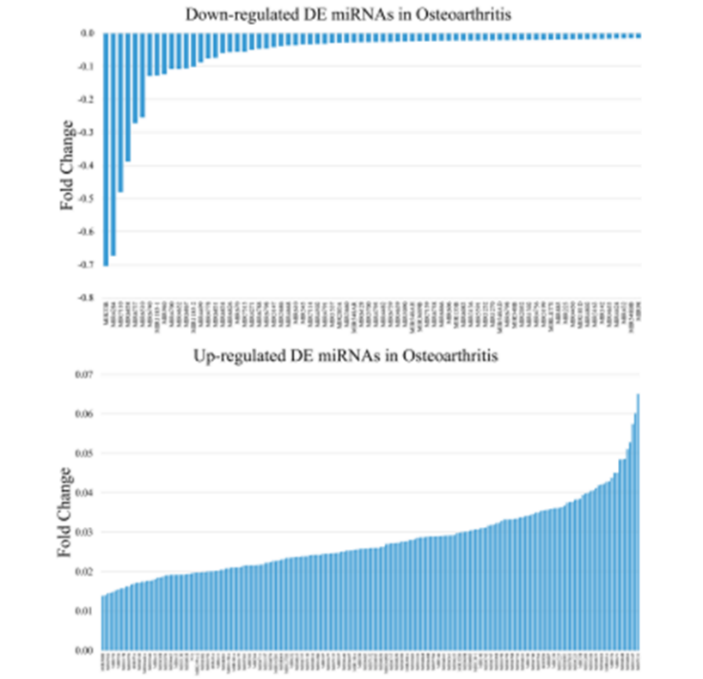
图释:Agilent Human miRNA芯片筛选差异表达的miRNAs上下调统计柱形图。
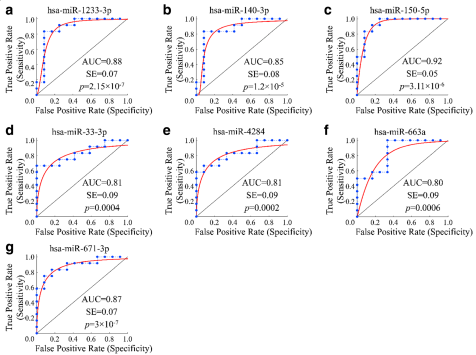
图释:ROC分析筛选OA相关生物标志物。
 图释:qPCR验证、靶基因预测及生信分析确定hsa-miR-140-3p,hsa-miR-671-3p和hsa-miR-33b-3p)用作评估的OA风险和进展的潜在的生物标志物。
图释:qPCR验证、靶基因预测及生信分析确定hsa-miR-140-3p,hsa-miR-671-3p和hsa-miR-33b-3p)用作评估的OA风险和进展的潜在的生物标志物。
→ microRNA Expression Profiles in Myocardium of High-Fat Diet-Induced Obesity Rat . Diabetes, Metabolic Syndrome and Obesity: Targets and Therapy . 2020
→ CircLONP2 enhances colorectal carcinoma invasion and metastasis through modulating the maturation and exosomal dissemination of microRNA-17 . Molecular Cancer . 2020
→ MiR-107 confers chemoresistance to colorectal cancer by targeting calcium-binding protein 39 . British Journal of Cancer . 2020
→ MicroRNA‑449a regulates the progression of brain aging by targeting SCN2B in SAMP8 mice . International Journal of Molecular Medicine . 2020
→ Down regulation of miR-542-3p promotes osteogenic transition of vascular smooth muscle cells in the aging rat by targeting BMP7 . Human Genomics . 2019
→ miRNAs deregulation in serum of mice is associated with lung cancer related pathway deregulation induced by PM2. 5 . Environmental Pollution . 2019
→ PinX1 represses renal cancer angiogenesis via the mir-125a-3p/VEGF signaling pathway . Angiogenesis . 2019
→ Knockdown of LncRNA SCAMP1 suppressed malignant biological behaviours of glioma cells via modulating miR‐499a‐5p/LMX1A/NLRC5 pathway . Journal of cellular and molecular medicine . 2019
→ Endothelial cell-derived small extracellular vesicles suppress cutaneous wound healing through regulating fibroblasts autophagy . Clinical Science . 2019
→ Exosomes derived from hypoxic epithelial ovarian cancer cells deliver microRNAs to macrophages and elicit a tumor-promoted phenotype . Cancer letters . 2018

